
2016年9月15日,《Genome Biology》报道了一种基于SGN的基因编辑新技术,以结构引导的内切酶(SGN,Structure-guided nuclease)实现体内外DNA任意序列的靶向和切割。论文一作为Shu Xu,论文通信作者为南京大学医学院附属金陵医院的周国华(Guohua Zhou)研究员、南京大学模式动物研究所的赵庆顺(Qingshun Zhao)教授和朱敏生(Minsheng Zhu)教授。做为基因编辑领域的从业者,读后很有感触,应BioArt主编之邀请,以半学术的方式、以随笔的形式写出,与各位分享,不严谨之处请大家各自消毒。
感触之一:构思巧妙,略有瑕疵,瑕不掩瑜。
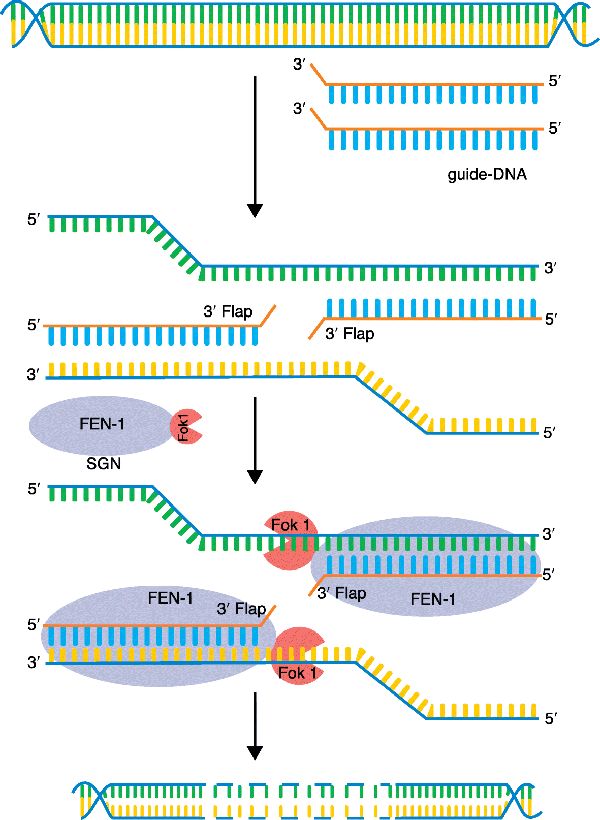
论文中,作者巧妙地融合FEN1(Flap endonuclease-1,是一种可以特异性识别flap结构的核酸内切酶,参与DNA的复制,修复和重组过程;除此之外它还具有双链DNA特异的5‘-3’的核酸外切酶活性)和已经被成功用于ZFN和TALEN的DNA剪切结构域Fok I,结合标准化的linker(GS repeats),设计了一个chimeric protein,实现了可编程的基因编辑系统,具有以下特点:短链ssDNA导向的基因组特定位置;编辑结果是产生大片段的deletion(可以大于2.6kb);可以在斑马鱼胚胎中成功编辑内源基因。这个构思,看得出包含ZNF以及TALEN的影子,其实这三者设计思路是一致的,其创新点在于靶向元件的选择十分巧妙,切割元件直接me too。令人惊喜的是,这种原创性工作出自我们中国科学家团队,略有遗憾的是,论文中体内靶点做的偏少,也没有以CRISPR或者TALEN为对照,导致尚不能够评估其相对低的编辑效率是来自位点特异性障碍还是来自技术本身(znf703基因编辑效率1/96≈1%;cyp26b1基因编辑效率是3/29≈10%、这个位点还真不低)。另外一点,如果SGN系统编辑结果是产生大片段的deletion,那么后期的同源重组做起来要相对困难(冒昧的揣测一下:FEN-1外切酶活性是否可以dead?貌似大片段的deletion应该是5′-3’的核酸外切酶活性引起的)。
感触之二:表述质朴谦逊,留下很大的优化空间。
通篇论文读下来,科学之外,还感觉到一种相对质朴的文风,措辞之间充盈着谦逊。这么讲,可能超出了学术范畴,所以称之为随笔,既然自己给自己开了这么一个后门,所以,干脆就谈出来,好在笔者与南京大学与作者没有关联,也就没有了套磁之嫌疑。例如,在基本术语上作者没有跟风:“SGN”而不是“ssDNA guided Nuclease”,“DNA editing”而不是“genome editing”,这些细节都能够体现出一种“独立性”。基因编辑技术的效率是极其重要的,目前看在这篇论文中,作者没有更多地报道相关的条件优化工作,例如效率瓶颈是存在于guide DNA与靶向区域的结合效率?还是存在于SGN的识别效率?整个生物学场景之中,目标区域的DNA melting究竟有多重要?是转录相关事件还是复制相关事件?(冒昧的揣测一下:是不是质粒编辑实验中采用可诱导启动子即可帮助判断?)当然,不应该要求一篇论文解决和回答这么多的科学或技术问题,但是可以预计,这个新工具可能还有较大优化空间,期待着他们更多的进一步报道。
感触之三:就是要挑战CRISPR,尽管它似乎难以逾越!
众所周知,今年5月2日《Nature Biotechnology》在线发表河北科技大学韩春雨博士“一鸣惊人”的论文,报告了一种NgAgo-gDNA基因编辑新工具,尽管因不可重复而使韩春雨“一波三折”地陷入学术诚信危机,但是,此文也算是高调地揭开了挑战CRISPR暗中竞赛的盖子。尽管CRISPR如日中天,甚至有“long live CRISPR”之类的戏言,但是,CRISPR并不完美,这种“不完美”不仅仅来自Off-target、PAM的限制性、难以实现单碱基精确编辑之类的技术瑕疵,更是来自人类对新技术的“天然贪婪”,来自根深蒂固的奥林匹克精神“更快、更高、更远”,来自我们骨子里的征服欲。正如哈佛大学医学院遗传学教授George Church所言:新技术都是脆弱的,随时可能被取代;加州大学圣迭戈分校的Prashant Mali 说的更直白“我们需要的不止这些”。所以,从技术使用者的角度看,CRISPR是大自然和几位先锋科学家送来的珍贵礼物,在欣然拥抱它的同时、当然也期待着更好的技术出现;从技术开发者的角度看,大红大紫般火热的CRISPR又是新的竞赛标杆,它令人嫉妒地、高傲地立在那里,挑逗和激发着人们超越它的冲动。
感触之四:源自天然、超越天然,从基因编辑技术演化史看“工程化”在技术工具开发中的重要性。
有人把基因编辑技术做了“断代工程”,给技术划代,很形象、也利于普及,但是有时候也比较困难。一般地,理论上可以在哺乳动物细胞中近乎任意位点切割并引发编辑的ZFN、TALEN以及CRISPR,它们在时间节点上依次出现、而且效率和便利性也越来越好,所以被称为第一代、第二代、第三代基因编辑技术(1G、2G、3G)。笔者愿意把他们称之为大众基因编辑工具,因为对应着的还有一些小众工具,鉴于其自身的技术局限和缺陷,并没有被大家普遍接受。今天,先聊一聊大众工具,随后加一些小花边,再聊聊那些正在被淘汰和被遗忘的小众工具,补充这些小众工具的演化史,可以更加清晰地看出技术发展脉络,或许从中获得另外的灵感和启发。
从大众工具看,“工程化”贯穿始终。现代中文语境中,一直有一种混淆科学与技术的“语义学”困境。科学与技术相关但不相同,有人形象地这样区分科学与技术:know what,know why是科学,know how是技术。基因编辑总体上是一种技术,其相关工具的开发,起步于科学发现,但是不止步于科学发现。例如,从现有公开文献看,CRISPR最重要的科学发现节点是2011年卡彭蒂艾(Emmanuelle Charpentier)对tracrRNA的生物学功能的阐明。但是,有时候,造物主很懒,他开辟了这个世界之随后可能置之不理了。所以,大自然留给我们的礼物,有时候配不上我们征服的野心,因此,就人类目标而言,我们从来都不吝啬和迟疑于改进和再造。果然,随后的2012年,卡彭蒂艾就会同詹妮弗·刀娜(Jennifer A. Doudna)联合发表了划时代论文,把tracrRNA和guide RNA合二为一,做成了工程化的“chimeric single guide”,sgRNA由此诞生。而在CRISPR-Cas工程化、模块化方面贡献最大的,应该首推华人科学家张锋教授。除CRISPRi、 CRISPRa之外,早在2013年的综述中,张锋教授就展望了包括把Cas设计为光控模式在内的各类工程化方案。而就是在本月,又推出了两项以遥控sgRNA的方式对CRISPR实施即时控制的技术方案。哈佛和神户大学的团队先后发表了利用“工程化”措施将AID与dCas9做成chimeric protein实现了不依赖于同源重组的单碱基编辑。就在本月初,MIT的团队创建了光敏感的sgRNA技术;几乎与此同时,深圳的科学家团队报告了“化学控制”的sgRNA的控制技术。
让我们把视野再回望到ZFN和TALEN,更是工程化的杰出案例,直至今天讨论的SGN,其“动作模块”甚至“毫不动摇”地使用FokⅠ,所变换进化的是“GPS定位模块”。这堪称技术演化之中还留下了历史痕迹,好似“保守序列”一样,让人惊叹“自然进化”与“人工进化”异曲同工之奇妙。
所以,基因编辑工具开发工程化的基本方程式是:GPS定位模块+执行模块。话分两头说。
先聊“执行模块”。FokⅠ屡战屡胜,但是,一定还有其它选择,毕竟,造物主应该是慷慨的,地球生命演化了四十亿年,留下的自然遗产极为丰富。
再聊聊GPS定位模块。这个模块工作效率及操作便利性如何,是基因编辑工具“好不好使”的关键。ZFN和TALEN的主要特点是:以蛋白质特定结构域来完成靶向定位,其主要缺陷是:定位模块体外准备麻烦,工作量大成本高;相比之下,CRISPR-Cas却方便的多,所以在总体竞争中胜出。但是CRISPR-Cas还是或多或少存在Off-target的弊端,为了解决这个问题、进一步强化定位精准性,已有报道以dcas9为定位器,融合上FokⅠ,实现正义链和反义链双向定位、并形成FokⅠ二聚体造成DNA双链断裂(DSB)、引发编辑。本次讨论的南京大学的这篇文章,再一次创新了GPS定位模块,首次采用FEN-1(flap endonuclease-1)来执行定位功能,将定位指令转化为方便人工编程的guide-ssDNA,做的很巧妙。
聊到这里,下一个创新近似于呼之欲出:尽管NgAgo似乎失败了,但是它工程化改造的前景呢?pAgo做为基因组“GPS定位模块”的可能性,怎能不令工具开发者怦然心动,就连我那个简陋的实验室,都已经于几个月前就开始努力了,万一大牛们漏掉了某些创意呢?
总之,GPS定位模块+执行模块=基因编辑工具,两个模块的重点是定位模块。设计灵感源自天然存在的自然遗产、但不止步于天然存在。自然界留给我们很多的提示和启发,例如:位点特异重组酶(site specific recombinase)如何?整合酶(integrases)如何?转座酶(transpotase)如何?其它未知的recombinase如何?这个领域的干法和湿法挖掘竞赛应该一直在进行。张锋曾说到:“通过对多种酶进行探索,我们可以得到一个更强的基因组编辑工具箱。我们必须继续探索未知。”
最后的花边:从G0谈起,回顾一下“沦落”为小众的基因编辑工具。
上世纪七十年代末,利用限制性内切酶实现了质粒体外重组,标志着第一代基因工程的诞生。随后,基于同源重组的体内染色体水平的基因工程成为现实,但是由于重组率极低,必须使用抗生素抗性或营养缺陷等标记加以筛选,做不到无痕编辑。之后,尽管发展了反向筛选标记、cre位点预埋及抗性回收等技术措施,但是,还是繁琐和低效。业界对无标记的无痕基因编辑技术是十分期待的,无标记无痕的关键在于编辑效率,只要效率达到百分之一以上的数量级别,就有希望。这里让我们一起回顾一下两个小众工具,作为“绿叶”来衬托一下广为人知的大众工具。
其一,G0代的重组工程(Recombineering)。上世纪90年代末,基于λ噬菌体的Red重组酶的重组工程(Recombineering)出现了,这个领域中,中国科学家于代冠(Daiguan Yu)跟随NIH的Donald L . Curt,做出了不少贡献,于代冠博士后来回到了中科院广州生物医药与健康研究院。基于Red系统,哈佛大学George Church于2008年在《Nature Biotechnology》上发表了改进版的MAGE,可以自动化地在数天内引发十亿计的突变;至2013年,Church又把基于ss-oligo的的重组工程从大肠杆菌扩展到酿酒酵母,这个过程还与rad51/rad54相关,被Church发展成YOGE技术,之所以特别强调Church,是因为这位伟大的科学家也是早期CRISPR的推进者之一,他采用Cas9编辑高等细胞基因组的论文,与张锋“同框”于2013年1月的Science。但是,重组工程最终没有能够再扩展到其它物种,特别是没有实现哺乳动物细胞的基因编辑。大肠杆菌的Red/ET系统,也是重组工程的重要实现工具,也是目前仍在普遍使用的分子生物学基本操作工具,这个系统源自中国科学家张友明在欧洲留学工作期间做出的开创性工作,张友明博士后来回到山东大学工作。总体上,基于寡核苷酸入侵的重组工程可扩展性不够好(局限于原核的细菌、真核最多跨到酿酒酵母),效率相对低下(在千分之一到百分之一之间),难以大幅度优化。
其二,G2.5代的Targetron。这个来自原核微生物防御机制的Targetron技术,笔者更愿意把它称之为2.5代技术,不是因为它的效率,而是因为它的GPS定位模块的工作方式,其方式是结合了“个别DNA位点的蛋白质识别”和“其它位点的RNA识别”,而且识别序列是可编辑的、可以“reprogrammable”的。这个编辑工具的大本营首推德克萨斯大学奥斯汀分校,他们有对外开放的设计软件及一些技术服务,但是,它编辑复杂、使用困难、物种可扩展性不高,梭状芽孢杆菌是可以用的,中科院微生物所李寅组和上海的杨晟组都有相关工作。总之,仍然是一个小众工具。
SGN将会如何?是小众工具还是能够发展成大众工具呢?pAgo能不能进一步W为NgAgo“正名”?能不能正名之后再发展成大众工具呢?前提是solid、可重复,并且用户友好。让我们拭目以待吧!
源于天然而超越天然,正道也!再次祝贺南京大学科学家在基因编辑领域的这项重大突破!(生物谷Bioon.com)
相关会议推荐

2016(第四届)非编码RNA研讨会
会议时间:2016.10.28-2016.10.29 会议地点:上海
会议详情:http://www.bioon.com/z/2016ncrna/

 基因君官网
基因君官网


















